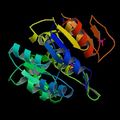
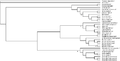
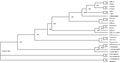
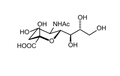
Uncategorized files
From MDWiki
Jump to navigationJump to search
Showing below up to 500 results in range #251 to #750.
- AM 06 08.pdf 0 × 0; 716 KB
- AM 07.01.pdf 0 × 0; 723 KB
- AM 07 01.pdf 0 × 0; 723 KB
- AM 07 01.pdf $wgFileExtensions = .pdf 0 × 0; 723 KB
- AM 07 03.pdf 0 × 0; 335 KB
- AM 07 04.pdf 0 × 0; 410 KB
- AM 07 05.pdf 0 × 0; 214 KB
- AM 07 06.pdf 0 × 0; 945 KB
- AM 08 01.pdf 0 × 0; 2.74 MB
- AM 08 02.pdf 0 × 0; 966 KB
- AM 08 03.pdf 0 × 0; 399 KB
- AM 08 04.pdf 0 × 0; 145 KB
- AM 08 05.pdf 0 × 0; 1.14 MB
- AM 08 06.pdf 0 × 0; 2.08 MB
- AM 08 07.pdf 0 × 0; 953 KB
- AM 08 08.pdf 0 × 0; 1.88 MB
- AM 08 09.pdf 0 × 0; 4.57 MB
- AM 91 01.pdf 0 × 0; 228 KB
- AM 95 02.pdf 0 × 0; 1.82 MB
- AM 95 03.pdf 0 × 0; 1.68 MB
- AM 95 04.pdf 0 × 0; 1.93 MB
- AM 95 05.pdf 0 × 0; 1.7 MB
- AM 95 06.pdf 0 × 0; 2.05 MB
- AM 95 07.pdf 0 × 0; 1.09 MB
- AM 96 01.pdf 0 × 0; 627 KB
- AM 96 02.pdf 0 × 0; 309 KB
- AM 97 01.pdf 0 × 0; 228 KB
- AM 98 01.pdf 0 × 0; 206 KB
- AM 98 02.pdf 0 × 0; 4.54 MB
- AM 98 03.pdf 0 × 0; 144 KB
- AM 98 04.pdf 0 × 0; 405 KB
- AM 98 06.pdf 0 × 0; 81 KB
- AM 98 07.pdf 0 × 0; 6.03 MB
- AM 99 02.pdf 0 × 0; 215 KB
- AM 99 03.pdf 0 × 0; 531 KB
- AM 99 04.pdf 0 × 0; 61 KB
- AM 99 05.pdf 0 × 0; 168 KB
- AM 99 06.pdf 0 × 0; 129 KB
- AM 99 07.pdf 0 × 0; 283 KB
- AM 99 08.pdf 0 × 0; 325 KB
- AS.gif 633 × 97; 5 KB
- AS2CFS.JPG 640 × 480; 20 KB
- AS3.JPG 307 × 493; 29 KB
- ASAcat1.png 643 × 584; 196 KB
- ASAgreen.png 552 × 615; 258 KB
- ASAsite.png 607 × 540; 172 KB
- ASAsite1.png 615 × 579; 183 KB
- ASK.png 508 × 450; 111 KB
- ASKhydro.png.jpg 728 × 592; 382 KB
- ASKsite.jpg 606 × 542; 203 KB
- ASKsite1.png 593 × 537; 214 KB
- ASKsite3.png 616 × 577; 225 KB
- ASKsite4.png 583 × 539; 220 KB
- ATPbinding.jpg 640 × 480; 278 KB
- Acession numbers for blast results.txt ; 256 bytes
- Acid.jpg 805 × 505; 237 KB
- Acobridgedhbond.jpg 517 × 531; 63 KB
- Active Site.JPG 640 × 480; 20 KB
- Active Site of 2cfsA.JPG 531 × 403; 17 KB
- Active site alignment.jpg 532 × 512; 54 KB
- Adenine modified.jpg 659 × 783; 25 KB
- Adenine modified1.jpg 658 × 323; 19 KB
- Adpribosemodel.jpg 962 × 421; 214 KB
- Alanwithteddy.jpg 1,141 × 794; 340 KB
- Alber AnnuRevBiochem08.pdf 0 × 0; 2.16 MB
- Ali.jpg 560 × 231; 39 KB
- Ali tensor comparison.pdf 0 × 0; 133 KB
- Alighn 2uved catalytic site.png 640 × 408; 118 KB
- Align2.txt ; 2.89 MB
- Align 2uvd.png 640 × 408; 165 KB
- Alignment.PNG 891 × 144; 9 KB
- Alignment.bmp 0 × 0; 1.62 MB
- Alignment.jpeg 1,001 × 565; 191 KB
- Alignment.jpg 1,001 × 565; 191 KB
- Alignment.txt ; 2.67 MB
- Alignment1.jpg 527 × 769; 67 KB
- Alignment1g3p.jpg 640 × 480; 63 KB
- AlignmentC.png 809 × 522; 36 KB
- AlignmentN.png 820 × 516; 36 KB
- Alignment 2.JPG 1,253 × 779; 417 KB
- Alignment 2ifu & 1qqe.JPG 640 × 580; 36 KB
- Alignment 3.JPG 576 × 834; 182 KB
- Alignment 4.JPG 586 × 834; 159 KB
- Alignment of Dali top 5.png 1,185 × 80; 41 KB
- Alignment picture.gif 732 × 369; 29 KB
- Alignment sequence 1.JPG 574 × 711; 153 KB
- Aligntment highlighted.PNG 1,228 × 639; 155 KB
- Aligntment translocation.PNG 1,418 × 547; 175 KB
- Aloy NatRevMolCellBiol2006.pdf 0 × 0; 735 KB
- Alpesh.JPG 768 × 768; 271 KB
- Alpesh lychee.png 258 × 399; 130 KB
- Alpha.jpg 58 × 20; 1 KB
- Alpha oxidation.JPG 622 × 447; 20 KB
- Alpha oxidation.jpg 500 × 638; 81 KB
- Am 02 02.pdf 0 × 0; 239 KB
- An2690.gif 70 × 52; 616 bytes
- AnnotatedMSA2str.jpg 3,184 × 1,937; 1.44 MB
- Annotated image1.jpg 640 × 434; 60 KB
- Annotatedimage.jpg 640 × 434; 60 KB
- Annotation.JPG 426 × 311; 30 KB
- Annotation.bmp 0 × 0; 389 KB
- Annotation1.JPG 760 × 689; 86 KB
- Applications of THz spectroscopy in biosystems.pdf 0 × 0; 982 KB
- Archeaon Carboxylesterase.PNG 438 × 484; 169 KB
- Artemisinin.png 300 × 300; 29 KB
- Arylformadisae reaction.gif 742 × 259; 5 KB
- Arylformamidase.txt ; 302 KB
- Arylformamidase alignment.jpg 1,116 × 524; 231 KB
- Arylformamidase alignment.png 800 × 376; 187 KB
- Arylformamidase function.jpg 445 × 111; 7 KB
- Arylformamidase the whole protein.PNG 584 × 599; 309 KB
- Assessment form.doc ; 43 KB
- Atb.png 300 × 131; 24 KB
- Atlas.png 520 × 790; 19 KB
- Atomic structures of amyloid cross-b.pdf 0 × 0; 2.96 MB
- Atp01.gif 419 × 373; 14 KB
- BLAST.png 658 × 562; 43 KB
- BLAST10.png 1,262 × 737; 692 KB
- Ba5125.pdf 0 × 0; 1.12 MB
- Back view.png 640 × 408; 141 KB
- Background alpesh.png 2,400 × 2,400; 632 KB
- BacterANDhomoTREE.jpg 1,237 × 733; 141 KB
- BacterCLUSTAL.aln ; 50 KB
- BacterTREE.jpg 856 × 621; 55 KB
- Baldauf TRENDS 2003.pdf 0 × 0; 161 KB
- Bash-Beginners-Guide.pdf 0 × 0; 1.16 MB
- Behind pocket.gif 640 × 480; 1.62 MB
- Behind pocket surface.gif 640 × 480; 3.15 MB
- Benjie1.PNG 439 × 402; 30 KB
- Benjie2.PNG 386 × 323; 16 KB
- Berendsen1981 SPC.pdf 0 × 0; 136 KB
- Berendsen1987 SPCE.pdf 0 × 0; 376 KB
- Binding.jpg 945 × 599; 77 KB
- Binding pocket.png 579 × 736; 97 KB
- Binding sites.JPG 961 × 854; 124 KB
- Bindingsite 2ifuA.png 698 × 729; 397 KB
- Bindsite1.jpg 384 × 384; 26 KB
- Bindsites2.PNG 1,064 × 733; 49 KB
- Biological Unit 2.jpg 250 × 250; 16 KB
- Biomosagain.jpg 794 × 1,163; 340 KB
- Blast.txt ; 1.03 MB
- Blast Results.jpg 596 × 591; 78 KB
- Blast hits.jpg 960 × 720; 139 KB
- Blast search vs uniprot.jpg 960 × 720; 99 KB
- Blasthp.jpg 923 × 97; 20 KB
- Blastp-Macaca mulatta.png 376 × 603; 43 KB
- Blastp.gif 572 × 338; 4 KB
- Blastp search-1ru8.png 399 × 615; 42 KB
- Blastresults.txt ; 387 KB
- Blue hills.jpg 800 × 600; 28 KB
- Boostrap.PNG 591 × 1,320; 34 KB
- Boostrap.png 591 × 1,320; 34 KB
- Bootstrap1.png 1,008 × 514; 39 KB
- Bootstrap Tree Alignment.jpg 1,280 × 998; 113 KB
- Bootstrap tree.jpg 1,201 × 632; 58 KB
- Bootstrap tree alignment.JPG 1,280 × 998; 107 KB
- Bootstrap tree final.jpg 1,920 × 1,200; 108 KB
- Bootstraptree.JPG 651 × 950; 85 KB
- Bootstraptreeunrooted.JPG 651 × 950; 75 KB
- Boottree.png 953 × 599; 41 KB
- Boron.png 424 × 600; 23 KB
- Bruhn2006 IntJQuantumChem106-2065.pdf 0 × 0; 211 KB
- Brute force schema.png 830 × 390; 13 KB
- Buchete JMB2005.pdf 0 × 0; 1.13 MB
- Bw28.jpg 731 × 402; 28 KB
- Byetta.jpg 320 × 240; 28 KB
- C-terminus of LOC144557.txt ; 94 KB
- CARBOXYLASE.PNG 830 × 699; 421 KB
- CAST-2nz2.PNG 937 × 563; 89 KB
- CAST-3bl5.PNG 996 × 569; 101 KB
- CASTp 2ob5 cl.jpg 610 × 400; 98 KB
- CASTp 2ob5 lig.jpg 614 × 400; 97 KB
- CASTp front.PNG 940 × 1,050; 132 KB
- CATALYTIC TRIAD 1.PNG 636 × 591; 356 KB
- CE pic.JPG 614 × 421; 32 KB
- COASYAcobridgedhbond.JPG 517 × 531; 63 KB
- COASYAcobridgedhbond.jpg 517 × 531; 63 KB
- COASYAcohydrophilic.JPG 820 × 771; 83 KB
- COASYAcohydrophilicres.JPG 1,216 × 39; 21 KB
- COASYAcohydrophobic.JPG 1,002 × 786; 100 KB
- COASYAcohydrophobicres.JPG 1,219 × 37; 21 KB
- COASYAcoother.JPG 993 × 778; 130 KB
- COASYAcootherres.JPG 1,216 × 36; 20 KB
- COASYBfactor.jpg 625 × 467; 47 KB
- COASYCleft table.jpg 796 × 386; 88 KB
- COASYClefts.jpg 593 × 488; 129 KB
- COASYCoa atomic struct.JPG 630 × 640; 90 KB
- COASYCoa atomic struct by bfactor.JPG 635 × 662; 68 KB
- COASYCompounds.JPG 593 × 695; 49 KB
- COASYConformationtypes.JPG 627 × 692; 45 KB
- COASYDali.txt ; 1.19 MB
- COASYHydro.jpg 509 × 426; 55 KB
- COASYHydro2.jpg 607 × 504; 39 KB
- COASYHydrophobicity.JPG 591 × 729; 37 KB
- COASYSecondary structure comparsion.jpg 1,215 × 480; 70 KB
- COASYSecondary structure with bind sites.gif 470 × 283; 7 KB
- COASYSeqcongif.gif 512 × 480; 1.98 MB
- COASYStructcongif.gif 512 × 480; 1.91 MB
- COASYStructconoriginal.wmv ; 1.91 MB
- COASYStructureconservationstructurealignment.JPG 8,884 × 253; 523 KB
- COASYTmhmm graph.gif 710 × 350; 3 KB
- COASYUnlbridgedbondh.JPG 993 × 763; 68 KB
- COASYUnlbridgedbondhres.JPG 1,219 × 37; 21 KB
- COASYUnlhydrophilic.JPG 1,002 × 702; 91 KB
- COASYUnlhydrophilicres.JPG 1,218 × 38; 20 KB
- COASYUnlother.JPG 949 × 520; 53 KB
- COASYUnlotherres.JPG 1,219 × 37; 20 KB
- COASYWatermolecules.JPG 584 × 746; 57 KB
- CR1.png 1,139 × 824; 882 KB
- CR2.png 1,129 × 744; 720 KB
- CR3.png 1,132 × 751; 625 KB
- Carboxylase.txt ; 2 KB
- Carboxylase A chain.PNG 640 × 512; 135 KB
- Carboxylase A chain.bmp 0 × 0; 960 KB
- Carboxylesterase Chain A.txt ; 2 KB
- Carboxylesterase reaction.gif 659 × 92; 2 KB
- Carboxylesterase reaction.png 659 × 92; 2 KB
- Carton pocket 1.png 640 × 480; 80 KB
- Cartoon.jpg 484 × 253; 44 KB
- Cartoon behind pocket 1.png 640 × 480; 79 KB
- Cat triad 1jji.PNG 418 × 496; 201 KB
- Cat triad red.PNG 694 × 648; 502 KB
- Catalytic Site of 2cftA.jpg 554 × 512; 36 KB
- Catalytic site.png 640 × 480; 192 KB
- Catalytic triad conversation.PNG 815 × 563; 30 KB
- Catalyticsite.png 640 × 434; 151 KB
- Cattriad 2c7b.PNG 477 × 438; 150 KB
- Chain.jpg 576 × 535; 28 KB
- ChainA.PNG 499 × 514; 193 KB
- ChainA1.PNG 499 × 514; 193 KB
- ChainA 1jji.PNG 438 × 484; 169 KB
- ChainA 2c7b.PNG 488 × 428; 133 KB
- Chain A.PNG 286 × 364; 89 KB
- Chain A.jpg 499 × 514; 193 KB
- Chang MscL-1998.pdf 0 × 0; 1.32 MB
- Chapter1 introduction.pdf 0 × 0; 4.04 MB
- Charge surface ani.gif 580 × 528; 5.43 MB
- Charlie.png 640 × 434; 87 KB
- Chemical reaction.JPG 640 × 512; 9 KB
- Chin natureMethods05.pdf 0 × 0; 245 KB
- Chloro.png 640 × 434; 99 KB
- Chocolatefish.jpg 129 × 50; 2 KB
- Cladogram.JPG 801 × 518; 38 KB
- Cladogram view.JPG 1,118 × 846; 126 KB
- Cleft Analysis 2cfsA.jpg 911 × 696; 85 KB
- Cleft Analysis 2oycA.jpg 905 × 720; 88 KB
- Cleft Analysis PyMOL 2cfsA V1.jpg 494 × 404; 42 KB
- Cleft Analysis PyMOL 2cfsA V2.jpg 433 × 429; 44 KB
- Cleft Analysis PyMOL 2oycA V1.jpg 456 × 381; 41 KB
- Cleft Analysis PyMOL 2oycA V2.jpg 463 × 403; 42 KB
- Cleft analysis 2i2O.jpg 0 × 0; 1.1 MB
- Clefts.JPG 1,059 × 850; 132 KB
- Clus.jpg 389 × 235; 20 KB
- Clustal.jpg 394 × 329; 21 KB
- Clustal1.jpg 1,282 × 377; 182 KB
- Clustal2.jpg 1,278 × 375; 194 KB
- Clustal3.jpg 1,276 × 387; 206 KB
- ClustalX-alignment.JPG 1,030 × 837; 336 KB
- ClustalX.jpg 1,203 × 618; 381 KB
- ClustalX image.JPG 1,203 × 618; 390 KB
- ClustalX omit.jpg 1,158 × 617; 339 KB
- Clustal 0-130.jpg 972 × 481; 113 KB
- Clustal 130-260.jpg 875 × 432; 124 KB
- Clustal 260-390.jpg 875 × 432; 131 KB
- Clustal 390-520.jpg 876 × 434; 133 KB
- Clustal 520-650.jpg 875 × 432; 110 KB
- Clustal Alignment top 5.txt ; 4 KB
- Clustal X.jpg 1,203 × 618; 381 KB
- Clustal results.jpg 970 × 483; 142 KB
- Clustalexample.JPG 366 × 270; 41 KB
- Clustalexample.bmp 366 × 270; 41 KB
- Clustalx.pdf 0 × 0; 1.24 MB
- Clustalx.png 859 × 1,320; 140 KB
- Clustalx1.JPG 838 × 572; 189 KB
- Clustalx1.jpg 0 × 0; 3.75 MB
- Clustalx1a.jpg 1,280 × 1,024; 438 KB
- Clustalx2.JPG 838 × 571; 208 KB
- Clustalx2.jpg 1,280 × 1,024; 475 KB
- Clustalx3.JPG 838 × 582; 218 KB
- Clustalx3a.jpg 1,280 × 1,024; 503 KB
- Clustalx4a.jpg 1,280 × 1,024; 444 KB
- Clustalx5a.jpg 1,280 × 1,024; 445 KB
- Clustalx6a.jpg 1,280 × 1,024; 482 KB
- Clustalx taken from residue 98-350.png 1,280 × 771; 118 KB
- Clustalx taken from residue 98-350 Part2.png 1,280 × 769; 112 KB
- Cluster.png 640 × 434; 143 KB
- Clustering methods.pdf 0 × 0; 1.88 MB
- Clutsalw1.JPG 941 × 831; 132 KB
- CoAA - Pantothenate kinase expression data (mouse).png 520 × 610; 14 KB
- CoAD reaction.gif 977 × 189; 5 KB
- CoAE reaction.gif 1,112 × 197; 5 KB
- CoA Synthesis localistion.png 520 × 610; 14 KB
- CoA Synthesis pathway.gif 454 × 372; 4 KB
- CoA structure.png 300 × 117; 25 KB
- CoA structure 2.png 300 × 126; 5 KB
- CoA synthase localisation.png 520 × 610; 14 KB
- CoAsy.jpg 700 × 700; 27 KB
- Coasy2f6rapredictedligandbindingsites.JPG 640 × 512; 31 KB
- CoasyCphmodelpredictedligandbindingsites.JPG 640 × 512; 33 KB
- CoasyPocketaco.JPG 1,136 × 756; 108 KB
- CoasyPocketunl.JPG 1,111 × 757; 111 KB
- Collaboration ven diagram.PNG 535 × 469; 11 KB
- Compar1.png 640 × 408; 89 KB
- Compar2.png 640 × 408; 93 KB
- Comparison 2ijz and 1vhe.JPG 942 × 299; 51 KB
- Comparison 2ijz and 1vhe sequence.JPG 576 × 627; 107 KB
- Comparison 2ijz and 1vhe sequence2.JPG 576 × 627; 107 KB
- Comparison 2ijz and 1xfo3.JPG 817 × 334; 52 KB
- Comparison 2ijz and 2cf4.JPG 1,066 × 312; 60 KB
- Comparison stuff (note ligands).jpeg 1,035 × 631; 133 KB
- Comparison stuff 2.jpeg 971 × 625; 99 KB
- Confidence.jpeg 1,093 × 288; 39 KB
- Confidence.png 533 × 473; 52 KB
- Confidence interaction with names.PNG 727 × 540; 72 KB
- Confidence interaction with names.png 727 × 540; 72 KB
- Conformation type of ERp18.png 592 × 425; 99 KB
- Connolly1983 JApplCrystallogr16-548.pdf 0 × 0; 1.49 MB
- Conres.jpg 757 × 595; 130 KB
- Conres.png 527 × 645; 123 KB
- Consense.jpg 1,887 × 1,187; 134 KB
- Consense.txt ; 33 KB
- Consensetree.jpg 1,887 × 1,187; 80 KB
- Conserved.JPG 593 × 819; 40 KB
- Conserved.jpg 512 × 384; 316 KB
- ConservedRegion 1.bmp 0 × 0; 4.47 MB
- ConservedRegion 1.png 1,024 × 687; 95 KB
- ConservedRegion 2.png 1,021 × 681; 89 KB
- ConservedRegion 3.png 1,024 × 685; 80 KB
- Conserved regions.JPG 420 × 475; 24 KB
- Conserved regions.jpg 640 × 480; 471 KB
- Conserved regions of 2ijz-A.JPG 422 × 401; 26 KB
- Conservedtext.JPG 420 × 518; 28 KB
- Convergence of sampling in protein simulations.pdf 0 × 0; 410 KB
- Cross.jpg 25 × 28; 1 KB
- Crystal Structure 2cfsA.jpg 240 × 226; 10 KB
- DALI2pbl.png 725 × 144; 9 KB
- DALI 2cfsA Updated.jpg 796 × 452; 116 KB
- DALI RESULT.txt ; 1.51 MB
- DAL HSLs.png 730 × 172; 12 KB
- DSCF1385.JPG 2,848 × 2,136; 1.59 MB
- DSCF1386.JPG 2,136 × 2,848; 1.49 MB
- DSCF1387.JPG 2,848 × 2,136; 1.57 MB
- DSC 0127.jpeg 276 × 354; 85 KB
- DSC 0127.jpg 276 × 354; 85 KB
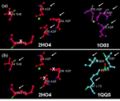
- Dali.PNG 925 × 724; 76 KB
- Dali.bmp 925 × 724; 1.92 MB
- Dali.jpg 1,008 × 247; 56 KB
- Dali33.PNG 760 × 603; 63 KB
- Dali Results.JPG 684 × 616; 142 KB
- Dali cutoff.jpg 976 × 287; 69 KB
- Dali output.jpg 721 × 345; 166 KB
- Dali output2.jpg 721 × 345; 89 KB
- Dali output3.jpg 721 × 345; 91 KB
- Dali results.png 653 × 333; 35 KB
- Dalii.PNG 760 × 603; 63 KB
- DanielTopology.gif 502 × 384; 9 KB
- DanielTopology2.gif 430 × 367; 19 KB
- Davis AngewChemIntEd03.pdf 0 × 0; 682 KB
- Davis DrugDiscovToday08.pdf 0 × 0; 1.52 MB
- Dehydrogenasereductase (SDR family) member 1 phylogram.png 835 × 608; 51 KB
- DesaltTrypticPeptide.pdf 0 × 0; 45 KB
- Directory structure 1.png 1,000 × 563; 152 KB
- Directory structure 2.png 1,000 × 563; 142 KB
- Directory structure 3.png 1,000 × 564; 77 KB
- Directory structure 4.png 1,000 × 563; 95 KB
- Distance Matrix Calcuation.txt ; 16 KB
- Document15 07.png 584 × 819; 27 KB
- Document17 01.png 1,189 × 426; 39 KB
- Document17 03.png 1,210 × 514; 45 KB
- Document18 01.png 807 × 160; 4 KB
- Document19 08.png 616 × 438; 59 KB
- Document20 01.png 740 × 509; 147 KB
- Document20 02.png 815 × 543; 97 KB
- Document2 01.png 784 × 458; 91 KB
- Document2 04.png 744 × 865; 666 KB
- Document2 05.png 229 × 145; 3 KB
- Document5 01.png 556 × 354; 7 KB
- Document6 01.png 1,214 × 652; 28 KB
- Document6 02.png 1,214 × 652; 29 KB
- Document7 01.png 1,214 × 652; 29 KB
- Document7 02.png 1,214 × 652; 75 KB
- Document7 03.png 1,214 × 682; 182 KB
- Document7 04.png 1,104 × 620; 50 KB
- Document7 05.png 1,214 × 652; 314 KB
- Document7 07.png 1,214 × 652; 94 KB
- Document7 11.png 1,214 × 652; 55 KB
- Document9 01.png 720 × 617; 489 KB
- Domain--1.jpg 361 × 345; 33 KB
- Domain--2.jpg 353 × 364; 50 KB
- Domain-1.jpg 510 × 510; 61 KB
- Domain.JPG 395 × 104; 7 KB
- Domain.jpg 804 × 696; 93 KB
- Domain1.jpg 357 × 175; 40 KB
- Domain111.jpg 640 × 400; 12 KB
- Domain2.JPG 395 × 104; 7 KB
- Domain arrangement.jpg 493 × 212; 88 KB
- Domain pic.jpg 448 × 304; 71 KB
- Domain pic2.jpg 512 × 384; 112 KB
- Domain pic3.jpg 512 × 384; 153 KB
- Domains.jpg 804 × 696; 53 KB
- Domains 2F6r.jpg 623 × 480; 30 KB
- Dotlet.PNG 508 × 336; 85 KB
- Doxorubicin bound surface POPC CLR bilayer.png 719 × 721; 1 MB
- DrosophilaVsHuman.png 600 × 300; 5 KB
- Drug Follow The Rules.pdf 0 × 0; 577 KB
- EIF4G w groove.JPG 512 × 384; 9 KB
- EIF4G w groove2.JPG 186 × 263; 7 KB
- EMI.jpg 0 × 0; 879 KB
- EMIi.jpg 343 × 336; 26 KB
- EPOR-EMP33 asu.png 1,181 × 816; 1.02 MB
- Edo4 ligand.JPG 762 × 783; 64 KB
- Electrostatic.gif 640 × 434; 4.14 MB
- Electrostatic potential.png 507 × 481; 229 KB
- Electrostatic potential (molecular surface).png 507 × 481; 229 KB
- Eskimos.jpg 104 × 104; 4 KB
- Esp.jpg 397 × 515; 24 KB
- Example.jpg 596 × 591; 78 KB
- Example1.jpg ; 131 KB
- Examplec.jpg 470 × 359; 25 KB
- Examplex.jpg 1,006 × 179; 30 KB
- Exp.jpg 520 × 790; 23 KB
- Export.png 1,463 × 848; 40 KB
- Expression.png 520 × 610; 13 KB
- Expression PHYHD1.png 520 × 790; 18 KB
- Expressionlev.jpg 640 × 724; 59 KB
- Expressionlev2.jpg 640 × 724; 63 KB
- External unifi order.png 987 × 796; 128 KB
- ExtractIDs.doc ; 302 KB
- FASTA.jpg 890 × 400; 94 KB
- FASTA.txt ; 249 bytes
- FASTA2.jpg 890 × 400; 99 KB
- FASTA2.txt ; 262 bytes
- FASTA fascin1 all.txt ; 56 KB
- Facscin broad bootstrap.jpg 802 × 588; 60 KB
- Fascin1 fasta.txt ; 1 KB
- Fascin CASTp back.PNG 936 × 1,050; 133 KB
- Fascin CASTp front.PNG 940 × 1,050; 132 KB
- Fascin bootstrap 500rep.jpg 1,159 × 852; 78 KB
- Fascin bootstrap animalia.insecta.jpg 933 × 845; 84 KB
- Fascin bootstrap animaliainsecta.jpg 933 × 845; 84 KB
- Fascin dali.PNG 925 × 724; 76 KB
- Fascin domains and conserved.png 640 × 434; 179 KB
- Fascin domains and conserved back.png 640 × 434; 178 KB
- Fascin electro back binding.PNG 640 × 480; 295 KB
- Fascin electro front binding.PNG 640 × 480; 317 KB
- Fascin movie.gif 640 × 434; 3 MB
- Fascin multiple alignment.jpg 1,184 × 562; 225 KB
- Fascin sec struc and domain.PNG 792 × 1,553; 116 KB
- Fascin secondary structure.png 640 × 480; 113 KB
- Fasta seq output of entrez.txt ; 31 KB
- Fewerseqforalign.txt ; 7 KB
- Fig1 chains.jpg 707 × 571; 66 KB
- Fig1 properties.JPG 962 × 1,112; 176 KB
- Fig1 properties.jpg 1,246 × 1,134; 233 KB
- Fig2.JPG 274 × 491; 24 KB
- Fig2 properties.jpg 960 × 535; 110 KB
- Fig3.JPG 445 × 757; 60 KB
- Fig3 Mg.jpg 1,042 × 491; 66 KB
- Fig4.JPG 415 × 939; 78 KB
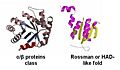
- Fig4 class&fold.jpg 469 × 272; 21 KB
- Fig5 MSA.jpg 958 × 960; 186 KB
- Fig6 residues.jpg 580 × 489; 33 KB
- Fig 1.bmp 0 × 0; 1.96 MB
- Fig 2.PNG 556 × 354; 7 KB
- Figtree.PNG 1,024 × 768; 257 KB
- Figure 1.png 561 × 549; 9 KB
- Figure 10.png 799 × 313; 91 KB
- Figure 11.png 803 × 419; 88 KB
- Figure 12.png 759 × 511; 116 KB
- Figure 13.png 762 × 600; 155 KB
- Figure 14.png 795 × 646; 128 KB
- Figure 15.png 758 × 640; 120 KB
- Figure 16.png 755 × 642; 127 KB
- Figure 17.png 403 × 87; 10 KB
- Figure 18.png 720 × 270; 62 KB
- Figure 19.png 1,211 × 713; 199 KB
- Figure 2.png 966 × 589; 146 KB
- Figure 3.png 338 × 596; 77 KB
- Figure 4.png 762 × 539; 107 KB
- Figure 5.png 756 × 579; 84 KB
- Figure 6.png 755 × 625; 83 KB
- Figure 7.png 755 × 743; 83 KB
- Figure 8.png 753 × 321; 58 KB
- File.jpg 0 × 0; 4.47 MB
- Final CoA synthesis pathway 2.gif 929 × 257; 73 KB
- Final fish eye tree.png 799 × 618; 93 KB
- First draft.JPG 652 × 917; 82 KB
- Flascin 1.jpg 596 × 591; 78 KB